Álgebra Lineal#

import matplotlib
import matplotlib.pyplot as plt
import numpy as np
import sympy
# Importar la biblioteca de álgebra lineal de SciPy
from scipy import linalg as la
# Módulo para resolver ecuaciones diferenciales ordinarias
from scipy.integrate import odeint
from scipy.sparse import linalg as splin
Operaciones de matrices y vectores#
Si A y B son dos matrices que se definen de la siguiente forma:
A = np.array([[3, 6, 2], [-4, 6, 1], [8, -2, 3]])
B = np.array([[4, 7, 1], [3, 4, 8], [9, 5, 6]])
La suma se realiza con en operador +.
A + B
array([[ 7, 13, 3],
[-1, 10, 9],
[17, 3, 9]])
En el caso de la multiplicación entre matrices NO se utiliza el operador *.
El mismo lo que efectúa es una multiplicación entre ndarray no entre matrices por lo
que resultará en \(c_{ij}=a_{ij}*b_{ij}\).
Para multiplicar matrices se utiliza la función np.matmul o el operador especial @ de la siguiente forma:
print("Multiplicación entre ndarrays:\n", A * B)
print("Multiplicación entre matrices:\n", A @ B)
print("O también\n", np.matmul(A, B))
Multiplicación entre ndarrays:
[[ 12 42 2]
[-12 24 8]
[ 72 -10 18]]
Multiplicación entre matrices:
[[48 55 63]
[11 1 50]
[53 63 10]]
O también
[[48 55 63]
[11 1 50]
[53 63 10]]
Pero además la multiplicación se pudiera expresar directamente como un producto interno
usando la función np.dot de la cual hablaremos seguidamente.
Sean las siguientes matrices \(A\) y \(B\) representadas en ndarrays:
A = np.arange(1, 7).reshape(2, 3)
A
array([[1, 2, 3],
[4, 5, 6]])
B = np.arange(1, 7).reshape(3, 2)
B
array([[1, 2],
[3, 4],
[5, 6]])
El producto dot entre dos matrices \(A_{M \times P}\) y \(B_{P \times N}\) se define como
\(\left(A \bullet B\right)_{M \times N}=\sum_{r=1}^{P}a_{ir}b_{rj}\).
Para ello se utiliza la función numpy.dot.
np.dot(A, B)
array([[22, 28],
[49, 64]])
np.dot(B, A)
array([[ 9, 12, 15],
[19, 26, 33],
[29, 40, 51]])
En el caso del producto dot entre una matriz y un vector \(A_{M \times N}\bullet \vec{v}_{N}=\sum\limits_{r=1}^{N}a_{ir}\vec{v}_{r}\), \(\forall i=1,\dotsc, M\) se puede implementar de la siguiente forma:
v = np.arange(3)
v
array([0, 1, 2])
np.dot(A, v)
array([ 8, 17])
También la función numpy.dot pudiera ser llamada desde la propia instancia del objeto ndarray de la siguiente forma:
A.dot(v)
array([ 8, 17])
La función numpy.inner no es más que la implementación del producto interno entre dos vectores.
Esta función está implícita en la función numpy.dot.
np.flip?
u = np.flip(v)
np.inner(v, u)
1
El producto externo entre dos vectores se define como \(x_{M}\bigotimes y_{N}=C_{M\times N}\) tal que \(c_{i,j}=x_{i}*y_{j}\), \(i=1,\dotsc,M\); \(j=1,\dotsc, N\).
x = np.array([1, 2])
y = np.array([3, 2])
np.outer(x, y)
array([[3, 2],
[6, 4]])
El producto de kronecker entre dos matrices
se obtiene a través de la función numpy.kron y retorna como resultado una matriz de bloques como sigue:
np.kron?
# Matriz de discretización del operador diferencial de la ecuación de Laplace
A = np.array([[4, 1], [1, 4]])
# Matriz identidad
I = np.eye(A.shape[0] * 3)
# Producto Kronecker
print("Matriz A\n", A)
print("Matriz I\n", I)
print("Producto Kronecker $I \\bigotimes A$\n", np.kron(I, A))
Matriz A
[[4 1]
[1 4]]
Matriz I
[[1. 0. 0. 0. 0. 0.]
[0. 1. 0. 0. 0. 0.]
[0. 0. 1. 0. 0. 0.]
[0. 0. 0. 1. 0. 0.]
[0. 0. 0. 0. 1. 0.]
[0. 0. 0. 0. 0. 1.]]
Producto Kronecker $I \bigotimes A$
[[4. 1. 0. 0. 0. 0. 0. 0. 0. 0. 0. 0.]
[1. 4. 0. 0. 0. 0. 0. 0. 0. 0. 0. 0.]
[0. 0. 4. 1. 0. 0. 0. 0. 0. 0. 0. 0.]
[0. 0. 1. 4. 0. 0. 0. 0. 0. 0. 0. 0.]
[0. 0. 0. 0. 4. 1. 0. 0. 0. 0. 0. 0.]
[0. 0. 0. 0. 1. 4. 0. 0. 0. 0. 0. 0.]
[0. 0. 0. 0. 0. 0. 4. 1. 0. 0. 0. 0.]
[0. 0. 0. 0. 0. 0. 1. 4. 0. 0. 0. 0.]
[0. 0. 0. 0. 0. 0. 0. 0. 4. 1. 0. 0.]
[0. 0. 0. 0. 0. 0. 0. 0. 1. 4. 0. 0.]
[0. 0. 0. 0. 0. 0. 0. 0. 0. 0. 4. 1.]
[0. 0. 0. 0. 0. 0. 0. 0. 0. 0. 1. 4.]]
Para calcular la inversa de una matriz se puede utilizar la función inv que está
implementada tanto en numpy.linalg.inv como en scipy.linalg.inv.
A = np.array([[1, -1], [2, 4]])
Ap = np.linalg.inv(A)
print("A=\n", A)
print("A' A=\n", np.dot(Ap, A))
print("A' A ~=\n", np.rint(np.dot(Ap, A)))
A=
[[ 1 -1]
[ 2 4]]
A' A=
[[1.00000000e+00 1.11022302e-16]
[0.00000000e+00 1.00000000e+00]]
A' A ~=
[[1. 0.]
[0. 1.]]
Ap = la.inv(A)
print("A' A ~=\n", np.rint(np.dot(Ap, A)))
A' A ~=
[[1. 0.]
[0. 1.]]
Veamos el siguiente ejemplo:
Supongamos que tenemos \(A_{M \times N}\), \(\Lambda_{M \times N}\) y \(B_{M \times N}\).
A = np.array([[1, -1], [2, 4]])
B = np.array([[-0.5, 1.0 / 3.0], [0.5, -2.0 / 3.0]])
L = np.diag([2.0, 3.0])
print("A=\n", A)
print("B=\n", np.round(B, 1))
print("L=\n", L)
A=
[[ 1 -1]
[ 2 4]]
B=
[[-0.5 0.3]
[ 0.5 -0.7]]
L=
[[2. 0.]
[0. 3.]]
y se desea realizar la siguiente operación: \(B\Lambda B^{-1}=A\). ¿Cómo se pudiera realizar en una sola línea de código?
print("B L B' = A =\n", np.matmul(B, np.matmul(L, la.inv(B))))
B L B' = A =
[[ 1. -1.]
[ 2. 4.]]
O utilizando el producto dot se puede plantear
print("B L B' = A =\n", np.dot(B, np.dot(L, la.inv(B))))
B L B' = A =
[[ 1. -1.]
[ 2. 4.]]
O utilizamos el símbolo @:
print("B L B' = A =\n", B @ L @ la.inv(B))
B L B' = A =
[[ 1. -1.]
[ 2. 4.]]
El tipo Matrix#
Las operaciones que realizamos en la sección anterior son todavía un poco extensas porque
son en realidad operaciones entre ndArrays.
Por tal motivo, en el módulo numpy existe una clase llamada matrix la cual encapsula las
propiedades y comportamientos de una matriz.
Con esta clase es posible hacer operaciones como estas:
A_ = np.matrix(A)
B_ = np.matrix(B)
L_ = np.matrix(L)
Ap_ = B_ * L_ * B_.I
print(Ap_)
[[ 1. -1.]
[ 2. 4.]]
de donde B.I calcula directamente la inversa de la matriz B.
También es posible hacer la transformación de la siguiente forma:
A_ = np.asmatrix(A)
print("Tipo de A_:", type(A_))
print("Tipo de A:", type(A))
Tipo de A_: <class 'numpy.matrix'>
Tipo de A: <class 'numpy.ndarray'>
Y de igual manera se puede transformar de una matrix a un ndarray.
Ap = np.asarray(Ap_)
print(Ap)
print("Tipo de Ap:", type(Ap))
[[ 1. -1.]
[ 2. 4.]]
Tipo de Ap: <class 'numpy.ndarray'>
Sistemas de ecuaciones#
Sistemas de ecuaciones cuadrados#
La resolución del problema: \(Ax=b\).
El módulo SymPy#
Este módulo de Python permite hacer cálculo simbólico lo cual es útil en muchos de los escenarios. Veremos algunos de sus usos en el álgebra lineal y concretamente en la resolución de sistemas de ecuaciones cuadrados.
sympy.init_printing() # Para imprimir los resultados de forma más estética
Creemos la matriz \(\begin{bmatrix} 2 & 3\\ 5 & 4 \end{bmatrix}\) utilizando el módulo sympy
A = sympy.Matrix([[2, 3], [5, 4]])
print("A=\n", A)
print("Tipo de A:", type(A))
A=
Matrix([[2, 3], [5, 4]])
Tipo de A: <class 'sympy.matrices.dense.MutableDenseMatrix'>
A

El rango de una matriz \(A\) indica la cantidad de vectores fila o columna linealmente independiente que forman parte de la matriz.
Si el rango no coincide con la dimensión de la matriz cuadrada \(A\), entonces se dice que tiene rango deficiente y la solución del sistema ya no será única en caso de tener.
A.rank()
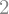
Por otra parte, la condición de la matriz permite saber si el problema es bien-planteado o no y así decidir cuáles son los mejores métodos a utilizar para su resolución.
\(\operatorname{cond}\left(a\right)\equiv \left\|A^{-1}\right|\|\bullet \left\|A\right\|\).
A.condition_number()
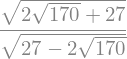
Claro que el número de condición anterior está dado de forma simbólica porque así es calculado por sympy. Para evaluarlo se usa
sympy.N(A.condition_number())
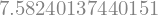
Si hablamos de la norma que sympy implementa por defecto es la norma de Frobenius
\(\left\|A\right\|_{F}=\sqrt{\sum_{i,j}\left|a_{ij}\right|^2}\).
A.norm()
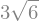
Para calcular otras normas usar el parámetro ord:
sympy.N(A.norm(2))
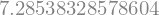
Tambien permite el cálculo de determinante
sympy.det(A)

A.det()

También es muy útil la función sympy.nullspace la cual devuelve el espacio nulo de la matriz:
El espacio no trivial en el cual \(\forall x: Ax=\vec{0}\).
A = sympy.Matrix(np.array([[1, -1], [2, 4]]))
A
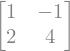
Calcular \((A - 2 I) x = \vec{0}\)
M = A - sympy.Matrix(np.diag([2.0, 2.0]))
M
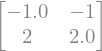
M.nullspace()
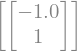
Y también \((A - 3 I) x = \vec{0}\)
M = A - sympy.Matrix(np.diag([3.0, 3.0]))
M
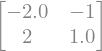
M.nullspace()
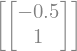
Más adelante veremos que son los valores y vectores propios de \(A\).
Descomposiciones de matrices y el cálculo simbólico#
Factorización \(A=LU\). Esta descomposición de una matriz \(A_{M\times N}\) está definida como \(PA=LU\), donde la \(P\) es una matriz de permutaciones, \(L\) una matriz triangular inferior (ceros por encima de la diagonal, unos en la diagonal y distinto de cero debajo de la diagonal) y \(U\) es una matriz triangular superior (ceros debajo de la diagonal).
Estas matrices son calculadas en el proceso de eliminación de Gauss. La descomposición \(LU\) se calcula reduciendo la matriz \(A\) a una matriz triangular superior.
Veamos como se puede realizar esta descomposición utilizando sympy:
A = sympy.Matrix([[4, 4, 8], [2, 8, 7], [1, 3, 6]])
A
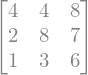
A.LUdecomposition()
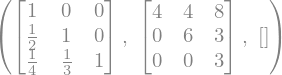
De esta forma se obtiene \(\left(L, U, P\right)\). En este caso no fue necesario ningún intercambio de ecuaciones por lo que la matriz \(P\) está vacía.
L, U, P = A.LUdecomposition()
L * U
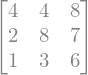
Si lo que se necesita es resolver el sistema entonces se pueden usar las siguientes variantes
b = sympy.Matrix([[1], [2], [1]])
b

A.solve(b)

O lo que sería lo mismo
A.LUsolve(b)

Evaluando la expresión anterior se obtiene:
sympy.N(_)
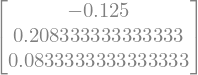
La factorización \(A = L L^T\) es un caso especial de la \(A = LU\). En este caso se explota el hecho que la matriz sea real simétrica y definida positiva para aplicar la descomposición de Cholesky.
La matriz \(L\) sigue siendo la matriz triangular inferior, pero en este caso la matriz \(U\) es igual a la transpuesta de \(L\). También está el caso de que \(LDL^T\) donde \(D\) es una matriz diagonal.
A = sympy.Matrix([[10, 2, 1], [2, 1, -2], [1, -2, 10]])
A
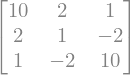
La matriz A es claramente simétrica. ¿Pero será definida positiva?
Para saberlo calculemos sus valores propios los cuales son reales y positivos en caso de que la matriz sea definida positiva.
A.eigenvals()
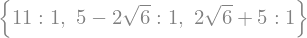
Cumpliéndose las condiciones podemos proceder a calcular la descomposición de Cholesky:
L = A.cholesky()
L
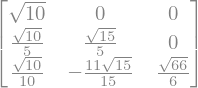
L.T
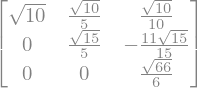
L * L.T
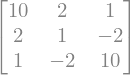
El módulo linalg de NumPy y SciPy#
Veamos cómo hacer las descomposiciones anteriores usando el módulo linalg de numpy y scipy.
Descomposición \(PA=LU\):
A = np.array([[4, 4, 8], [2, 8, 7], [1, 3, 6]])
P, L, U = la.lu(A)
print("P=\n", P)
print("L=\n", L)
print("U=\n", U)
P=
[[1. 0. 0.]
[0. 1. 0.]
[0. 0. 1.]]
L=
[[1. 0. 0. ]
[0.5 1. 0. ]
[0.25 0.33333333 1. ]]
U=
[[4. 4. 8.]
[0. 6. 3.]
[0. 0. 3.]]
Para resolver un sistema de ecuaciones se utiliza la siguiente función
b = np.array([[1], [2], [1]])
la.solve(A, b)
array([[-0.125 ],
[ 0.20833333],
[ 0.08333333]])
En el caso de la descomposición de Cholesky
A = np.array([[10, 2, 1], [2, 1, -2], [1, -2, 10]])
L = la.cholesky(A, lower=True)
print("L=\n", L)
print("A = L L.T =\n", np.matmul(L, L.T))
L=
[[ 3.16227766 0. 0. ]
[ 0.63245553 0.77459667 0. ]
[ 0.31622777 -2.84018779 1.3540064 ]]
A = L L.T =
[[10. 2. 1.]
[ 2. 1. -2.]
[ 1. -2. 10.]]
Métodos iterativos#
Ejemplo:
Método del gradiente conjugado. Este es elegible cuando:
La matriz es simétrica y definida positiva.
La matriz es simétrica y no definida positiva, pero bien condicionada.
La matriz no es simétrica, pero es bien condicionada.
A = np.array([[2, 3], [5, 4]])
b = np.array([4, 3])
la.solve(A, b)
array([-1., 2.])
Definiendo función delegado para calcular error en cada iteración del método
# Solución conocida
s = np.array([-1.0, 2.0])
# Almacenar resultado por iteración
iterationes = []
# Almacenar el error en cada interación
norm_dif = []
# Definición del método delegado o "callback" que será
# ejecutado en cada una de las interaciones del método
def delegate(xk):
iterationes.append(xk)
norm_dif.append(np.linalg.norm(s - xk))
Una implementación del método del gradiente conjugado se encuentra en
splin.cg(A, b, maxiter=1000, tol=1e-6, callback=delegate)
/tmp/ipykernel_1788/1622869473.py:1: DeprecationWarning: 'scipy.sparse.linalg.cg' keyword argument `tol` is deprecated in favor of `rtol` and will be removed in SciPy v1.14.0. Until then, if set, it will override `rtol`.
splin.cg(A, b, maxiter=1000, tol=1e-6, callback=delegate)
(array([-0.99999724, 1.99999715]), 0)
iters = np.arange(len(iterationes))
fig = plt.figure(figsize=(10, 8))
plt.grid()
plt.plot(iters, norm_dif, "k-", lw=2, label="Norma del error")
plt.xlabel(r"Iteraciones", fontsize=18)
plt.ylabel(r"$\left\|s_{k}-s^{\ast}\right\|_{2}$", fontsize=18)
# plt.xlim(-5, 240)
# plt.ylim(-0.3, 2.5)
plt.legend(loc=1, fontsize=18)
plt.title("Norma del error vs iteraciones")
plt.show()
plt.close()
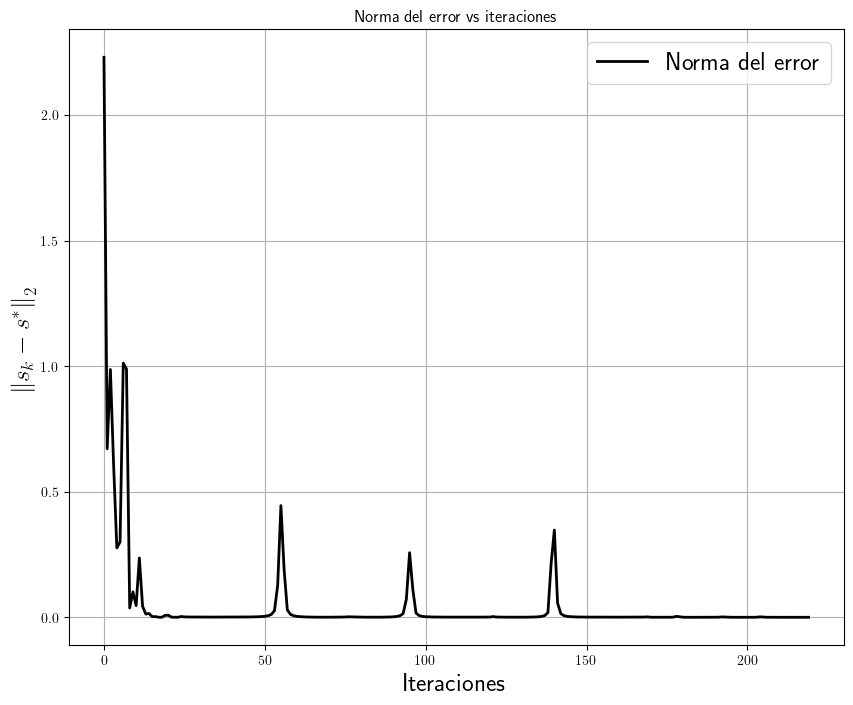
El problema de convergencia del método radica en que la matriz no es ni simétrica ni definida positiva. Sus valores propios son \(\lambda_{1}=-1\) y \(\lambda_{2}=7\). Si no son todos positivos no se cumple la condición de definida positiva.
Veamos que ocurre si los:
A = np.array([[3, 1, 0], [1, 3, 1], [0, 1, 3]])
A
array([[3, 1, 0],
[1, 3, 1],
[0, 1, 3]])
b = np.array([4.0, 5.0, 4.0])
b
array([4., 5., 4.])
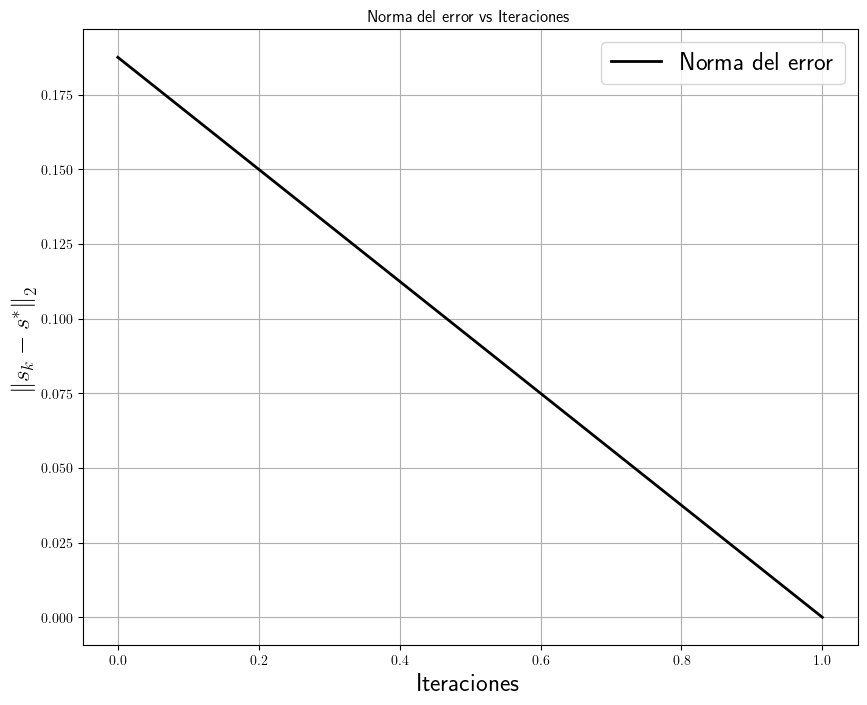
Sus valores propios esta vez son todos positivos: \(\lambda_{1}=1.58578644\), \(\lambda_{2}=3\) y \(\lambda_{3}=4.41421356\).
s = np.array([1.0, 1.0, 1.0])
# Almacenar resultado por iteración
iterationes = []
# Almacenar el error en cada interación
norm_dif = []
splin.cg(A, b, maxiter=1000, tol=1e-6, callback=delegate)
/tmp/ipykernel_1788/1622869473.py:1: DeprecationWarning: 'scipy.sparse.linalg.cg' keyword argument `tol` is deprecated in favor of `rtol` and will be removed in SciPy v1.14.0. Until then, if set, it will override `rtol`.
splin.cg(A, b, maxiter=1000, tol=1e-6, callback=delegate)
(array([1., 1., 1.]), 0)
iters = np.arange(len(iterationes))
fig = plt.figure(figsize=(10, 8))
plt.grid()
plt.plot(iters, norm_dif, "k-", lw=2, label="Norma del error")
plt.xlabel(r"Iteraciones", fontsize=18)
plt.ylabel(r"$\left\|s_{k}-s^{\ast}\right\|_{2}$", fontsize=18)
# plt.xlim(-5, 240)
# plt.ylim(-0.3, 2.5)
plt.legend(loc=1, fontsize=18)
plt.title("Norma del error vs Iteraciones")
plt.show()
plt.close()
También existen implementaciones de los métodos iterativos usuales:
splin.cgs(A, b, maxiter=1000, tol=1e-6)
/tmp/ipykernel_1788/884326417.py:1: DeprecationWarning: 'scipy.sparse.linalg.cgs' keyword argument `tol` is deprecated in favor of `rtol` and will be removed in SciPy v1.14.0. Until then, if set, it will override `rtol`.
splin.cgs(A, b, maxiter=1000, tol=1e-6)
(array([1., 1., 1.]), 0)
splin.bicg(A, b, maxiter=1000, tol=1e-6)
/tmp/ipykernel_1788/326691840.py:1: DeprecationWarning: 'scipy.sparse.linalg.bicg' keyword argument `tol` is deprecated in favor of `rtol` and will be removed in SciPy v1.14.0. Until then, if set, it will override `rtol`.
splin.bicg(A, b, maxiter=1000, tol=1e-6)
(array([1., 1., 1.]), 0)
splin.gmres(A, b, maxiter=1000, tol=1e-6)
/tmp/ipykernel_1788/974662482.py:1: DeprecationWarning: 'scipy.sparse.linalg.gmres' keyword argument `tol` is deprecated in favor of `rtol` and will be removed in SciPy v1.14.0. Until then, if set, it will override `rtol`.
splin.gmres(A, b, maxiter=1000, tol=1e-6)
(array([1., 1., 1.]), 0)
Análisis de sensibilidad#
Sea el siguiente sistema:
\(\begin{bmatrix} 1 & \sqrt{p}\\ 1 & \frac{1}{\sqrt{p}} \end{bmatrix} \begin{bmatrix} x_1\\ x_2 \end{bmatrix} = \begin{bmatrix} 1\\ 2 \end{bmatrix}\)
p = sympy.symbols("p", positive=True)
A = sympy.Matrix([[1, sympy.sqrt(p)], [1, 1 / sympy.sqrt(p)]])
b = sympy.Matrix([1, 2])
A
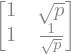
x = A.solve(b)
x
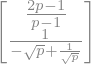
El problema es que en la medida que \(p\) se aproxime al valor \(1\) entonces la matriz \(A\) se vuelve singular. Esto hace que \(A\) sea una matriz mal condicionada.
A_cond = A.condition_number().simplify()
A_cond
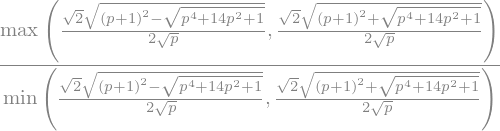
A_cond.subs(p, 1)

A_cond.subs(p, 1 + 1e-10)

A_cond.subs(p, 1.5)
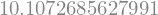
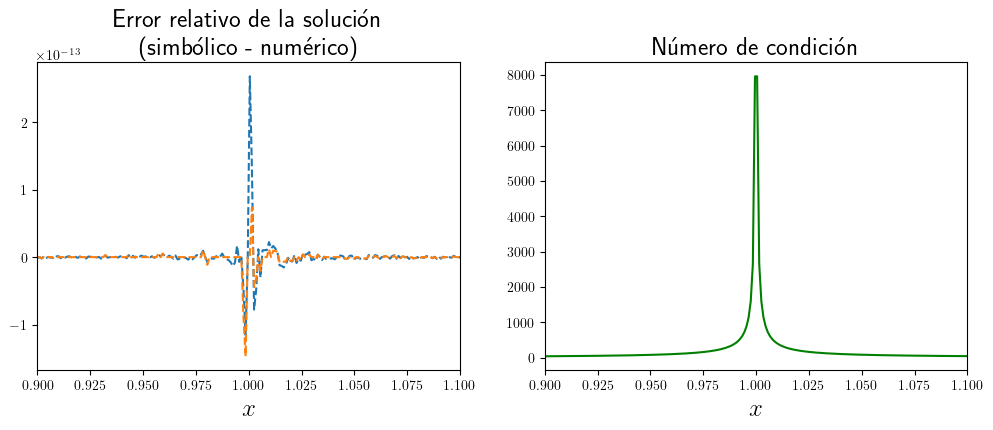
Hagamos un análisis numérico del problema. El siguiente código resolverá el sistema para un valor dado de \(p\).
AA = lambda p: np.array([[1, np.sqrt(p)], [1, 1 / np.sqrt(p)]])
bb = np.array([1, 2])
x_num_sol = lambda p: np.linalg.solve(AA(p), bb)
x_sym_sol = x
# Valores de prueba
p_vec = np.linspace(0.9, 1.1, 200)
fig, axes = plt.subplots(1, 2, figsize=(12, 4))
# Calcular error relativo
for n in range(2):
x_sym = np.array([x_sym_sol[n].subs(p, pp).evalf() for pp in p_vec])
x_num = np.array([x_num_sol(pp)[n] for pp in p_vec])
axes[0].plot(p_vec, (x_num - x_sym) / x_sym, "--")
axes[0].set_title("Error relativo de la solución\n(simbólico - numérico)", fontsize=18)
axes[0].set_xlabel("$x$", fontsize=18)
axes[0].set_xlim(0.9, 1.10)
# Condición de la matriz
axes[1].plot(p_vec, [A_cond.subs(p, pp).evalf() for pp in p_vec], "-g")
axes[1].set_title("Número de condición", fontsize=18)
axes[1].set_xlabel("$x$", fontsize=18)
axes[1].set_xlim(0.9, 1.10)
plt.show()
plt.close()
Sistemas de ecuaciones rectangulares#
x_vars = sympy.symbols("x_1, x_2, x_3")
A = sympy.Matrix([[1, 2, 3], [4, 5, 6]])
x = sympy.Matrix(x_vars)
b = sympy.Matrix([7, 8])
A
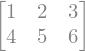
b

x

sympy.solve(A * x - b, x_vars)
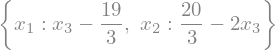
Problemas de valores y vectores propios#
El problema de los valores y vectores propios se refiere a la solución del problema \(A\vec{v}=\lambda\vec{v}\).
Referencia documental:
Implementación en SciPy: https://docs.scipy.org/doc/scipy/reference/generated/scipy.linalg.eig.html
Implementación en NumPy: https://numpy.org/doc/stable/reference/generated/numpy.linalg.eig.html
Por supuesto que pudiera pensarse en diagonalizar la matriz para simplificar el problema, pero esto cambia los valores propios cosa que no es deseable.
En su lugar se reagrupan los términos para tener \(\left(A-\lambda I\right)\vec{v}=0\) lo cual permite un mejor análisis. Obviando la solución trivial \(\vec{v}=0\), entonces nos enfocamos en el determinado por el polinomio característico \(\det\left(A-\lambda I\right)=0\).
Las raíces de este polinomio permiten conocer los valores propios \(\lambda\) y a partir de ellos los espacios de vectores propios asociados que conforman el espacio nulo de la matriz resultante \(\left(A-\lambda I\right)\vec{v}=0\).
En el módulo linalg de scipy se encuentran algunas funciones que permiten calcular los
vectores y valores propios de forma eficiente (usando rutinas implementadas en la biblioteca LAPACK de FORTRAN).
función |
Descripción |
|---|---|
|
Calcula los valores propios de un problema ordinario o generalizado (ver ejemplos debajo) de valores propios. |
|
Calcula los valores propios como el anterior, pero también brinda los vectores propios asociados (contiguos si vienen en pares). |
|
Realiza la misma función que el anterior, pero con la particularidad de que está optimizado para matrices simétricas. La implementación en |
|
Resuelve el problema para matrices simétricas tridiagonales (interesante en el área de las ecuaciones diferenciales en derivadas parciales). |
Demo #1: Veamos un ejemplo de un problema ordinario donde se tiene una matriz \(A=\begin{bmatrix}0 & -1\\1 & 0\end{bmatrix}\).
A = np.array([[0.0, -1.0], [1.0, 0.0]])
print("Valores propios ", la.eigvals(A))
Valores propios [0.+1.j 0.-1.j]
Al calcular los valores propios, estos son números complejos.
Como posible aplicación se puede decir que sus vectores propios asociados definen transformaciones rotatorias en el espacio.
Demo #2: Si calculamos un problema general donde definimos otra transformación lineal \(B=\begin{bmatrix}0 & 1 \\1 & 1\end{bmatrix}\), entonces se tiene el siguiente problema \(A\vec{v}=\lambda B\vec{v}\), \(\left(A-\lambda B\right)\vec{v}=0\).
En el siguiente ejemplo se muestra como resolver este problema.
B = np.array([[0.0, 1.0], [1.0, 1.0]])
print("Valores propios ", la.eigvals(A, B))
Valores propios [ 1.+0.j -1.+0.j]
En este caso los valores propios son números reales.
Demo #3: Supongamos ahora que queremos calcular además los vectores propios asociados.
Entonces podemos utilizar la función general scipy.linalg.eig:
A2 = np.array([[1, -1], [2, 4]])
# Calculando valores y vectores propios
e = la.eig(A2)
print("Valores propios:", e[0])
print("Vectores propios normalizados:\n", e[1] / la.norm(e[1]))
Valores propios: [2.+0.j 3.+0.j]
Vectores propios normalizados:
[[-0.5 0.31622777]
[ 0.5 -0.63245553]]
En este acaso se devuelve un array con dos elementos [valores propios, vectores propios].
En el caso anterior el polinomio característico queda \(\lambda^{2}-5\lambda+6=0\) con soluciones
\(\lambda_{1}=3\) y \(\lambda_{2}=2\).
Si se calculan analíticamente los espacios de vectores propios se obtiene \(\vec{v}_{\lambda_1}=\begin{bmatrix}-\frac{1}{2} \\\frac{1}{2}\end{bmatrix}\) y \(\vec{v}_{\lambda_2}=\begin{bmatrix}\frac{1}{3} \\-\frac{2}{3}\end{bmatrix}\).
Es importante notar que la función scipy.linalg.eig tiene los parámetros left y right.
Esto significa que
Si
left=True, entonces la matriz de vectores propios \(S\) dada será de acuerdo a \(A=S\Lambda S^{-1}\).Si
right=True, entonces la matriz de vectores propios \(S\) dada será de acuerdo a \(A=S^{-1}\Lambda S\).
La diferencia que se muestra en el segundo vector está dada por aproximaciones numéricas.
Ejercicios#
Ejercicio #1: Resolviendo sistema de ecuaciones con descomposición LU#
Dado el siguiente sistema de ecuaciones
# Creando matriz A
A = np.array([[1, 4, 5], [6, 8, 22], [32, 5, 5]], dtype=np.float64)
# Creando vector b
b = np.array([1, 2, 3])
Descompóngalo en las matrices \(P\), \(L\) y \(U\) e imprímalas:
# Calculando la descomposición LU
P, L, U = la.lu(A)
print("P =\n", P)
print("L =\n", L)
print("U =\n", U)
P =
[[0. 0. 1.]
[0. 1. 0.]
[1. 0. 0.]]
L =
[[1. 0. 0. ]
[0.1875 1. 0. ]
[0.03125 0.54424779 1. ]]
U =
[[32. 5. 5. ]
[ 0. 7.0625 21.0625 ]
[ 0. 0. -6.61946903]]
¿Es \(A\) «igual» a \(LU(A)\)?
Utilice la función np.allclose para ello o la norma de la diferencia entre matrices con una tolerancia de \varepsilon=1e-10.
print("¿Es A 'igual' a LU(A)?", np.allclose(A, P @ L @ U))
print("También ||A - PLU(A)|| =", la.norm(A - P @ L @ U) < 1e-10)
¿Es A 'igual' a LU(A)? True
También ||A - PLU(A)|| = True
Calcule el determinante de la matriz \(A\) usando la función la.det.
la.det(A)
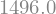
Calcule ahora el determinante de la matriz \(A\) utilizando la descomposición
\(LU\) de \(A\) sin usar la función det.
Recuerde que el determinante de una matriz es igual a la multiplicación de los determinantes de su descomposición.
Tenga en cuenta también las permutaciones contenidas en la matriz \(P\).
detL = 1.0
detU = np.prod(np.diagonal(U))
swaps = (np.diagonal(P).size - np.sum(np.diagonal(P))) - 1
detP = np.power(-1, swaps)
print("Determinante de A =", detP * detL * detU)
Determinante de A = 1495.9999999999998
Ejercicio #2: Calculando inversa de la matriz A utilizando la descomposición \(LU\)#
Para calcular la matriz inversa de \(A\) seguiremos el algoritmo basado en la propiedad \(AA^{-1}=I\) donde
\(A=\begin{bmatrix}a_{00}&\dots&a_{0n}\\ \vdots&\ddots&\vdots\\ a_{n0}&\dots&a_{nn}\end{bmatrix}\) y \(A^{-1}=\begin{bmatrix}\sigma_{00}&\dots&\sigma_{0n}\\ \vdots &\ddots &\vdots\\ \sigma_{n0} &\dots &\sigma_{nn}\end{bmatrix}\), la cual cumple que \(\begin{bmatrix}a_{00}&\dots&a_{0n}\\ \vdots &\ddots &\vdots\\ a_{n0}&\dots&a_{nn}\end{bmatrix} \begin{bmatrix} \sigma_{0j} \\ \vdots \\ \sigma_{n, j} \\ \end{bmatrix} = I_j \, j = 0, \dots, n \)
donde \(I_{j}\) es la columna j-ésima de la matriz identidad.
Y para ello vamos a aprovechar los beneficios que nos brinda la descomposición \(LU\) de la siguiente forma:
Primero que todo descompongamos \(A\) en las matrices \(PA=LU\). Entonces la columna \(j\)-ésima de la matriz inversa se calcula resolviendo el siguiente sistema
\(LU \begin{bmatrix} \sigma_{0 j} \\ \vdots \\ \sigma_{n, j} \\ \end{bmatrix} = P I_j \).
Calcule las columnas de la matriz \(A^{-1}\) implementando los siguientes algoritmos de «sustitución hacia adelante» y «sustitución hacia atrás»:
Sustitución hacia adelante:
\(\quad y_{i}=\dfrac{\left(I_{ij}-\sum\limits_{j=0}^{i-1}l_{ij}y_j\right)}{l_{ii}}\) para \( i=0,1,\dots,n\)
def forward_substitution(L, Pb):
# Inicializar la variable y que es igual a Ux.
y = np.zeros_like(Pb, dtype=np.double)
# Por cada fila despejar todas las variables y coeficientes que
# estén situados delante de la diagonal (que tiene valor 1)
# hacia el miembro derecho y dividirlo por el coeficiente de la
# diagonal que es 1. HINT: Para ello utilice el producto interno.
for i in range(0, L.shape[0]):
y[i] = Pb[i] - np.dot(L[i, :i], y[:i])
return y
Sustitución hacia atrás:
\(A^{-1}_{ij}=\dfrac{\left(y_{i}-\sum\limits_{k=i+1}^{n}u_{i k}A^{-1}_{ik}\right)}{u_{ii}}\)
donde el índice \(j\) se refiere a la columna j-ésima de la matriz \(A^{-1}_{ij}\) y el índice \(k\) es utilizado por el algoritmo para referirse a las columnas de \(U\).
def back_substitution(U, y):
# Iniciar la variable x con zeros del mismo tamaño que y
x = np.zeros_like(y, dtype=np.double)
# Por cada fila en orden inverso, se despejan las variables y
# coeficientes que estén situados detrás de la diagonal.
# Dividir por el valor del elemento en la diagonal.
# HINT: Usar el producto interno.
for i in range(U.shape[0] - 1, -1, -1):
x[i] = (y[i] - np.dot(U[i, i:], x[i:])) / U[i, i]
return x
Calculando la inversa de la forma:
\(LU A^{-1}_{j} = P I_{j}\)
para lo cual hacemos la sustitución
\(U A^{-1}_{j} = y_{j}\) y quedaría
\(L y_{j} = P I_{j}\) que pudiera ser resulto con el algoritmo de sustitución hacia adelante.
Luego, sustituimos el valor de \(y_j\) en la ecuación anterior resolviendo
\(U A^{-1}_{j} = y_{j}\)
utilizando el algoritmo de sustitución hacia atrás obteniendo la columna \(A^{-1}_{j}\) de la matriz inversa de A.
Implemente este algoritmo.
# Crear matriz identidad
I = np.identity(A.shape[0])
# Crear matriz inversa resultante inicialmente vacía
A_1 = np.empty_like(I)
# Iterar por las columnas de la matriz A_1
for j in range(A_1.shape[1]):
# Hacer sustitución hacia adelante (L y = P I_j)
y = forward_substitution(L, P @ I[:, j])
# Hacer sustitución hacia atrás (U x = y)
x = back_substitution(U, y)
# Reemplazar columna de la matriz inversa
A_1[:, j] = x
# Calcular inversa de A usando la función del módulo scipy.linalg para comprobación
Ap_1 = la.inv(A)
# Imprimir los resultados
print("A_-1 =\n", A_1)
print("inv(A) =\n", Ap_1)
# Comparar los resultados
print("A_-1 == inv(A)?", np.allclose(A_1, Ap_1))
A_-1 =
[[-0.04679144 0.00334225 0.03208556]
[ 0.45053476 -0.10360963 0.00534759]
[-0.15106952 0.08221925 -0.01069519]]
inv(A) =
[[-0.04679144 0.00334225 0.03208556]
[ 0.45053476 -0.10360963 0.00534759]
[-0.15106952 0.08221925 -0.01069519]]
A_-1 == inv(A)? True
